Mise en œuvre d'une méthode de docking moléculaire sur Google Cloud Platform
Le contexte
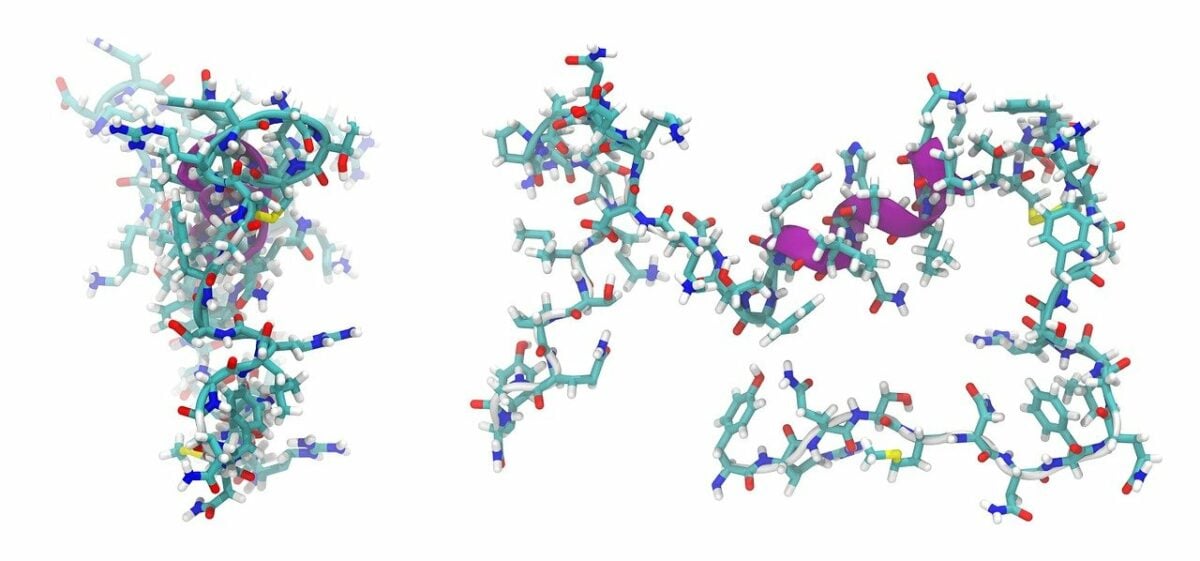
Dans le domaine de la modélisation moléculaire, l’amarrage (en anglais docking) est une méthode qui calcule l’orientation préférée d’une molécule vers une seconde lorsqu’elles sont liées pour former un complexe stable (voir la définition de l’amarrage moléculaire).
Aneo et l’Université Paris Diderot ont mis en œuvre une méthode de docking moléculaire sur Google Cloud Platform (GCP) afin d’analyser la faisabilité technique d’une migration vers le cloud et ses avantages en termes de temps de résultat.
Le défi
Un calcul de docking moléculaire peut prendre entre 20 secondes et 10 minutes avec une moyenne de 5 minutes pour un seul ordinateur. La bibliothèque moléculaire de l’Université Paris Diderot contient 7,2 millions de composés.
Le criblage de l’ensemble de la base de données et l’obtention d’une solution prendraient 68,5 ans avec un unique ordinateur. Pour être utile à l’industrie pharmaceutique, la méthode de criblage virtuel doit être beaucoup plus rapide.
La solution
La rareté et le coût nous empêchent d’utiliser les serveurs de calcul haute performance, « supercalculateur », comme outil de simulation de la bibliothèque de docking moléculaire. Les technologies cloud fournissent aux utilisateurs une infrastructure partagée, virtuellement illimitée et à la demande, permettant un changement de paradigme.
Il est désormais possible de créer automatiquement et de manière transparente un nouveau supercalculateur pour chaque nouvelle soumission et cela en réduisant les coûts. L’exécution est ainsi plus facile, plus rapide et moins coûteuse.
Les résultats
Un ordonnanceur développé sur la base de services gérés surveille en permanence le nombre de tâches en attente afin de provisionner la bonne quantité de nœuds de calcul pour traiter toutes les tâches à un moment donné. Les nœuds sont automatiquement désalloués dès qu’ils deviennent inactifs. Nous avons validé cette solution sur GCP, en criblant 10000 docking moléculaires sur 850 coeurs de calculs en 1 heure au lieu de 833 heures sur un seul coeur.
En conclusion, le passage des simulations de docking moléculaire sur GCP a permit de raccourcir de 34 jours à 1 heure les temps de calculs.
Vous souhaitez travailler avec nous ?
Confiez votre problématique à nos experts et devenez notre prochain cas clients.
Ces cas clients peuvent aussi vous intéresser


.png)
